La PCR se trata de una técnica que permite obtener copias de ADN de manera rápida y sencilla, como si se tratara de una verdadera fotocopiadora de muestras de ADN que se quieran amplificar.
Así, la reacción en cadena de la polimerasa (PCR), desarrollada en 1986 por Kary Mullis (premio Nobel en 1993, según él, idea potenciada en su pensamiento gracias a otras siglas: LSD), permite sintetizar en pocas horas millones de copias de un segmento de ADN a partir de una muestra muy pequeña.
Para ello se necesita:
- El ADN que se quiere amplificar (deben conocerse los extremos) para que se sinteticen cebadores complementarios que limiten el fragmento a copiar.
- Desoxiribonucleótidos trifosfato.
- ADN cebador (también llamados primers o sondas) complementario a las secuencias del ADN que flanquean el gen a copiar. Se necesita un cebador directo y otro indirecto, es decir, uno complementario a la secuencia del gen de una hebra (por ejemplo, la que va de 5´→3´) y el otro cebador complementario a la hebra de ADN complementaria (la que iría de 3´→5´).
- ADN polimerasa resistente al calor, procedente de la bacteria termófila Thermus aquaticus (Taq-polimerasa) o de la Archaea Pyrococus furiosus (Pfu polimerasa) si se requiere una mayor precisión.
Así, toda esta mezcla se deposita en eppendorffs (unos tubitos de laboratorio muy pequeños) que se colocan en el termociclador (aparato que lleva a cabo la PCR), el cual sigue procesos cíclicos de calentamiento y enfriamiento, según el siguiente procedimiento:
- Desnaturalización del ADN: se calienta la muestra por encima de los 90º para que se separen las hebras.
- Hibridación con los cebadores, primers o sondas: se baja la temperatura hasta 50ºC para que los cebadores hibriden con los extremos complementarios de cada cadena.
- Polimerización de las nuevas cadenas: se eleva la temperatura a 72ºC y la ADN polimerasa de alta temperatura (Taq polimerasa) sintetiza ADN.
- Acaba el ciclo y la temperatura baja a las condiciones estándar.
- Se repite los pasos 1-4, tantas veces como se requiera.
Puesto que en cada ciclo se duplica la cantidad de ADN existente, repitiendo este ciclo unas veinte veces, al tener una tendencia exponencial, se pueden obtener hasta un millón de copias del fragmento de ADN.

PCR: reacción en cadena de la Polimerasa. Observa, cómo primero desnaturalizamos el ADN (separamos ambas hebras por el aumento de la temperatura), posteriormente se produce la hibridación con el cebador que delimita el fragmento de ADN a amplificar y, finalmente, se produce la copia de las hebras por la acción de la polimerasa. Se repite el ciclo tantas veces como haga falta.
ELECTROFORESIS APLICADA A LA PCR
Una vez que se ha completado una reacción de PCR, necesitamos poder ver los resultados.
La interpretación de estos se nos puede complicar si hemos añadido varios cebadores que amplifiquen diferentes partes del ADN, como en una PCR multiplex o tengamos varias muestras a analizar, como el diagnóstico de varias personas con posible infección vírica (por ejemplo esa PCR que debíamos de hacer si éramos contacto estrecho con un enfermo de SARS-CoV-2).
Para ello, se carga una muestra de la mezcla de PCR en un gel de agarosa para electroforesis, el cual contiene una matriz de poros que le permite separar fragmentos de ADN en función de sus tamaños.
Para su movimiento a través del gel se aplica un campo eléctrico (una diferencia de potencial o voltaje). Así, el ADN, al estar cargado negativamente, se mueve hacia el polo positivo o ánodo.
En su viaje a tal polo positivo, aquellas muestras más grandes quedarán retenidas en los poros del gel y se depositarán al comienzo de su camino, mientras que las más pequeñas quedarán más abajo (más próximas al ánodo).
Así, teñimos los fragmentos de ADN con un marcador fluorescente y los vamos cargando o depositando en los diferentes pozos del gel, aplicamos la diferencia de voltaje y a esperar los resultados.
Igualmente, debemos de reservar algunos pozos para las muestras control y, por supuesto, un marcador de peso molecular (fragmentos de tamaño conocido que nos permita extrapolar, por comparación, el tamaño de nuestro fragmento de ADN).
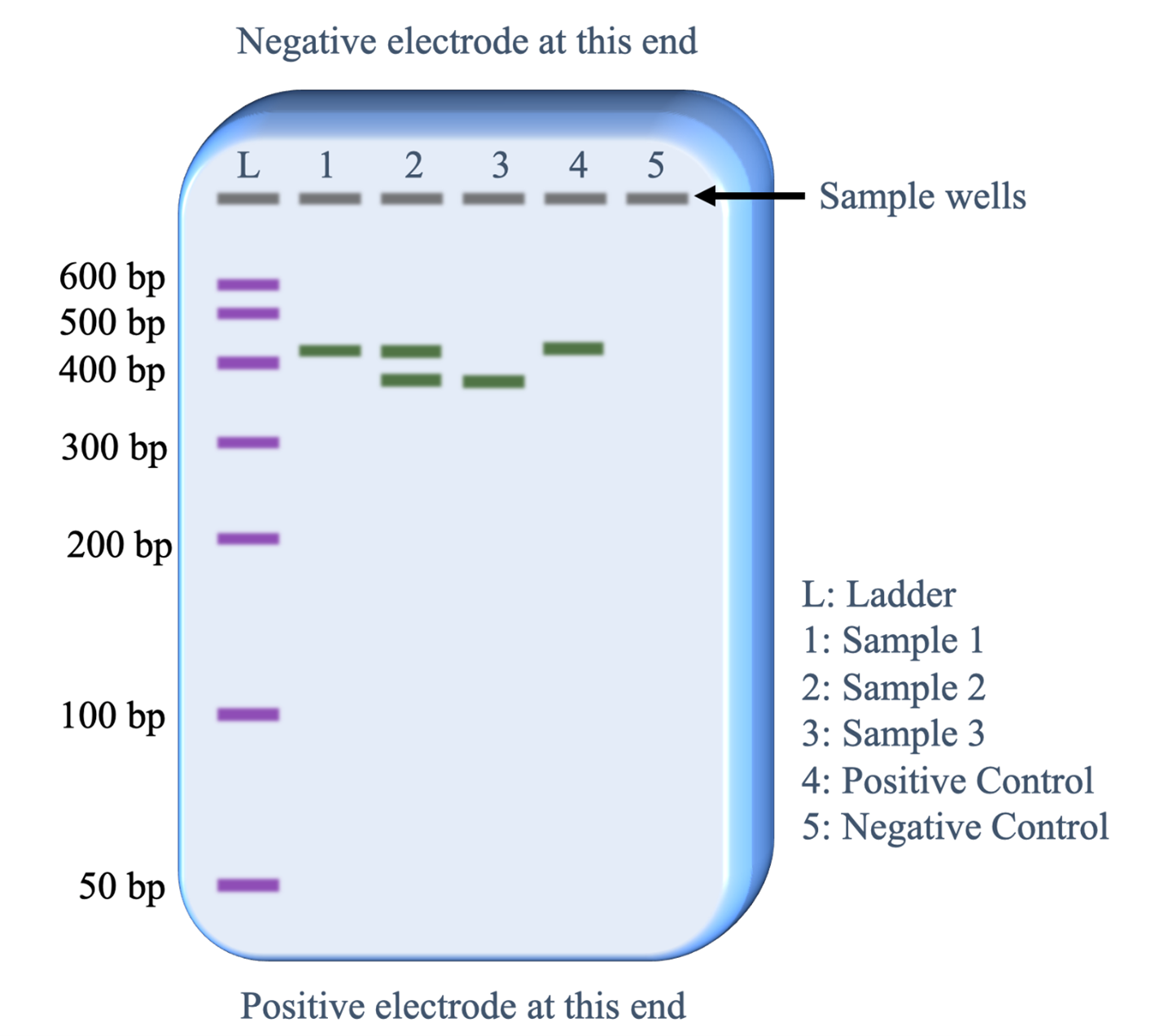
Electroforesis en gel de agarosa. Observa cómo los fragmentos de ADN migran a lo largo del gel y van hacia el polo positivo. Igualmente, los fragmentos de un menor peso molecular (más pequeños) migrarán más, mientras que los más grandes quedarán retenidos más arriba. También encontramos que tenemos una serie de pozos reservados para las muestras control y para el marcador de peso molecular, señalado por una letra «L».
APLICACIONES DE LA PCR
Las aplicaciones de la PCR son múltiples:
- Amplificaciones de ADN para todo tipo de estudios evolutivos o, paleontológicos, lo que le permitió a Svante Paabo ganar el Premio nobel de fisiología el año 2022.
- La obtención de la huella genética de ADN en medicina forense, pruebas de paternidad, etc.
- Detección de ADN para pruebas de diagnóstico, por ej., detección de virus en etapas tempranas de infección del VIH o en el SARS-CoV-2.